pro45.pdf
Anuncio

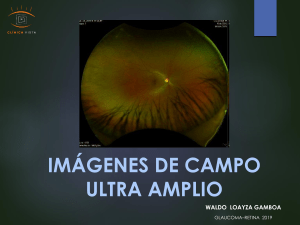
PROTEÓMICA Número 8, Febrero 2012 Pósters S1: Proteómica Cuantitativa P5 Expresión proteica diferencial de tratamiento de fotocoagulación con laser en células ARPE Carolina de la Torre1, Luna Martín1, Núria Colomé1, Joan-Josep Bech1, Bodil Israelsson2, Carl-David Agardh2, Elisabet Agardh2, Rafael Simó3, Francesc Canals1 1 Laboratori de Proteòmica, Vall d’Hebron Institute of Oncology (VHIO, Barcelona); 2 Unit on Vascular Diabetic Complications, Department of Clinical Sciences, Malmö, Lund University, 3 Diabetes and Metabolism Research Unit, Institut de Recerca Hospital Universitari Vall d’Hebron, Barcelona [email protected] La fotocoagulación con láser es una terapia rutinaria para el tratamiento de pacientes diabéticos con edema macular y retinopatía. Los mecanismos exactos involucrados en los beneficios de esta terapia son poco conocidos. La fotocoagulación con láser se realiza para sellar los vasos sanguíneos anormales o dañados y evitar que pierdan líquido y sangre. La fotocoagulación afecta al epitelio pigmentario de la retina (RPE) y se cree que este tejido es el que puede estar involucrado en el resultado terapéutico. En este estudio se ha utilizado un modelo de células humanas de epitelio pigmentario de la retina (ARPE), que han sido irradiadas con laser simulando las condiciones del tratamiento de fotocoagulación. Se ha comparado el perfil de expresión proteica de las células ARPE, bajo condiciones de alta y baja concentración de glucosa, con y sin tratamiento laser. El objetivo es conocer los mecanismos moleculares que podrían estar involucrados en los procesos de regeneración de las células de retina y los específicos en pacientes con diabetes. Para el análisis cuantitativo hemos utilizado la técnica de marcaje isobárico iTRAQ. Los péptidos marcados se fraccionaron mediante isoelectroenfoque “off-gel” para disminuir la complejidad de la muestra. Las fracciones fueron posteriormente analizadas por LC-MSMS. Para la comparación de las diferentes condiciones, con varias réplicas biológicas de cada condición, se ha utilizado un diseño experimental que incluye un pool de todas las muestras como patrón interno. Se han identificando y cuantificado alrededor de dos mil proteínas, de las cuales varias de ellas son especificas de cada condición. 83